"Biomasse per Laserscan"
03KB037 - Entwicklung von automatisierten
Biomasse-Analyse-
und Bewertungsinstrumenten auf Basis von Laserscan-Rohdaten
am Bsp. von Süddeutschland und bundesweiten Fallstudien
Prof. Dr. Klaus Schmieder
Dipl.-Biol. Alfons Krismann
|
Wie lässt sich das Biomasse-Potenzial einer Region, speziell von Offenland-Gehölzen erfassen? Und wie lässt sich eine bundesweite Vergleichbarkeit dieser regionalen Daten sicherstellen? Um Antworten auf diese Fragen zu finden, werden in dem Projekt unter Federführung des Instituts für Landschafts- und Pflanzenökologie an der Universität Hohenheim anwendungsnahe automatisierte Fernerkundungs-Instrumenten zur Erfassung und Typisierung von Landschaftspflegeholz und Brachflächen entwickelt und in einem nächsten Schritt das Biomassepotenzial berechnet. Als Datengrundlage werden flugzeug-gestützte Laserscanning-Daten verwendet, die in guter Auflösung bis zum Jahr 2013 komplett für die Landesflächen von Deutschland vorliegen werden. Im Rahmen des Projekts werden Modellrechnungen und Szenarien mit logistischen und geräte-technischen Kennwerte und Marktpreisen kombiniert. Auf der Grundlage von flugzeug-gestützten Laserscanning-Daten für regionale Fallstudien in vier Bundesländern (Nordrhein-Westfalen, Bayern, Niedersachsen und Brandenburg) werden die Biomasseanalysen exemplarisch aufbereitet. Die generierten Kataster ermöglichen eine direkte Berechnung dieser Biomasse-Vorräte (keine Schätzungen). Als Hilfsmittel werden Anwender-Tools entwickelt, z.B. der Aufbau einer Gehölzdatenbank, die die wesentlichen Auswertungen automatisieren. Als Werkzeug für die Praxis wird ein Landschaftspflegeholz-Verfügbarkeitstool (gemeindebezogen, auf Basis einer GIS-Gehölzdatenbank) und ein Logistikkostenrechner für konkrete Standorte für Abnehmer von Landschaftspflegeholz (i.d.R. Hackschnitzelkessel-Standorte) entwickelt. Der Projektpartner Prof. Dr. Krystek (Hochschule München) befasst sich mit der Entwicklung von Algorithmen für eine Typisierung und Biomasse-Bestimmung der Offenland-Gehölze und Brachland sowie der Überprüfung der zugrunde liegenden statistisch-empirischen Modelle (statistische Feldeichung). Ein Schwerpunkt bildet dabei die Einzelbaumdelinierung in Offenland-Gehölzen mit Full-Waveform Daten und Multispektraldaten (inkl. Datenfusion). Ziele: Projektträger: Projektträger Jülich [http://www.ptj.de/geschaeftsfelder/umwelt] Zuwendungsgeber: Bundesministeriums für Umwelt, Naturschutz und Reaktorsicherheit BMU Partner:
Universität Hohenheim
Prof. Dr. Klaus Schmieder
– Projektleiter Alfons Krismann
Hochschule für angewandte
Wissenschaften Prof. Dr. Peter Krzystek
– Projektleiter Matthias Rentsch Publikationen:
|
Visualisierte Zwischenergebnisse
Beispiel eines Referenzgehölzes: Eichenwäldchen mit Haselunterwuchs (Regen/Bayerischer Wald)
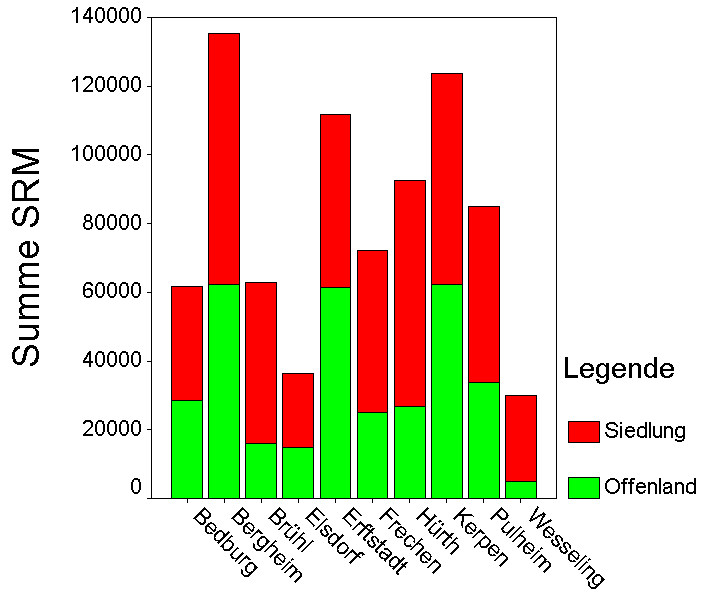
Abb. 1: Foto vom Sommer 2010.
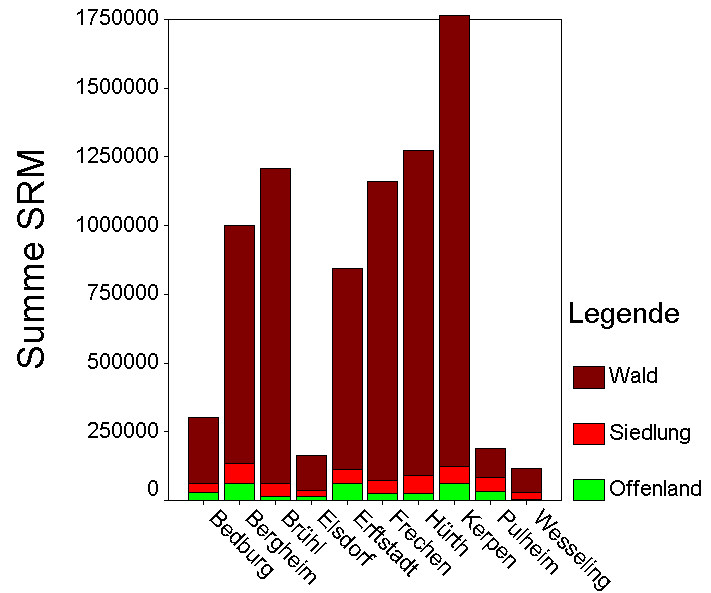
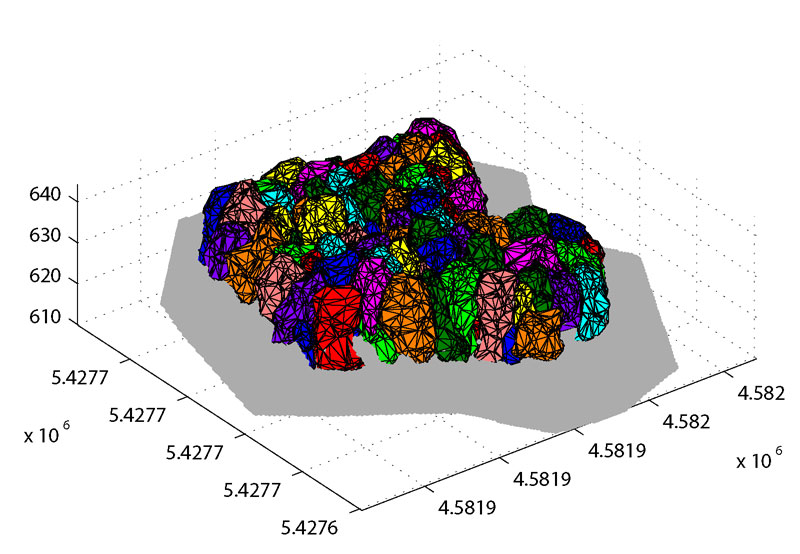
Abb. 2: Punktwolke eines terrestrischen Laserscanners: ca. 6 Millionen 3D-Einzelpunkte mit Farbwerten.
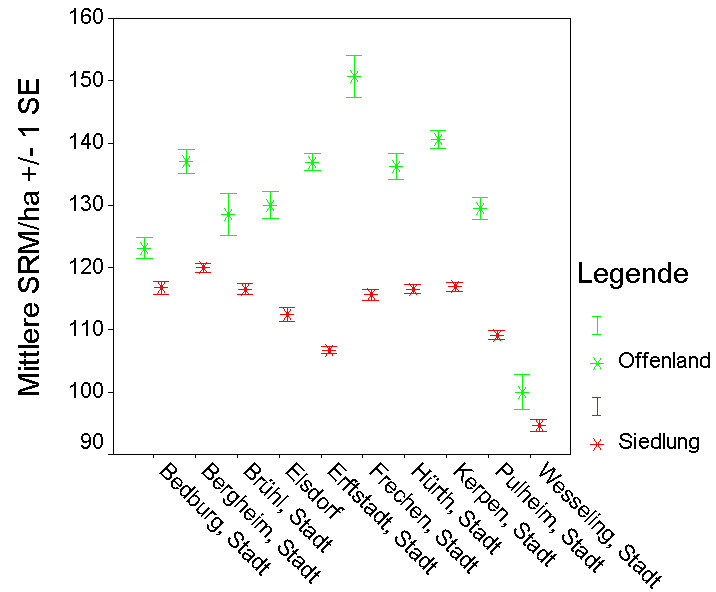
Abb. 3: Punktwolke eines Full Waveform Laserscanners: ca. 82.000 klassifizierte 3D-Einzelpunkte.
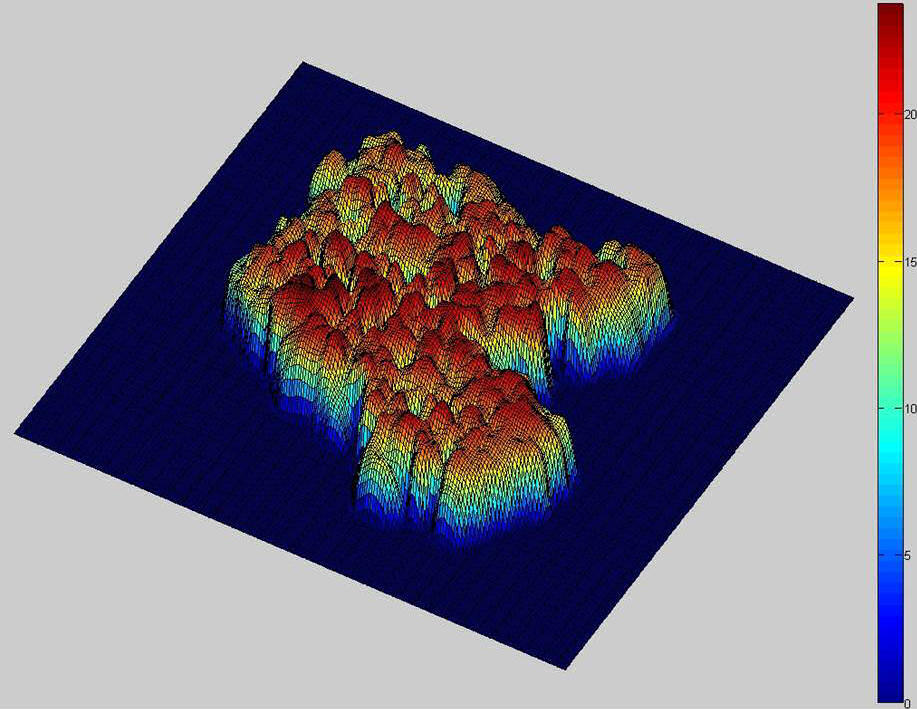
Abb. 4: Normalisiertes Oberflächenmodell (Höhen in [m]) berechnet aus 3D-Punkten eines terrestrischen Laserscanners.
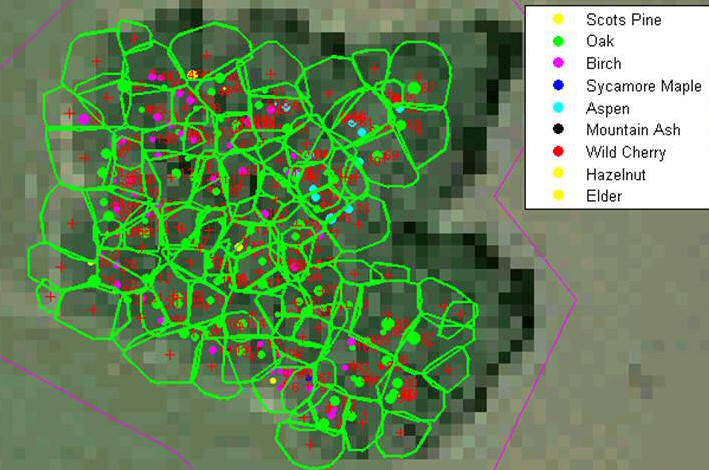
Abb. 5: 3D Normalized Cut Segmentierung von Bäumen mit Bestimmung der lokalen Maxima (rote Kreuze) auf Basis von 3D-Punkten eines Full Waveform Laserscanners.

Abb. 6: Visualisierung und Berechnung des Grünvolumens der segmentierten Gehölze mittels "Alpha-Shapes" (Full Waveform Laserscanner).
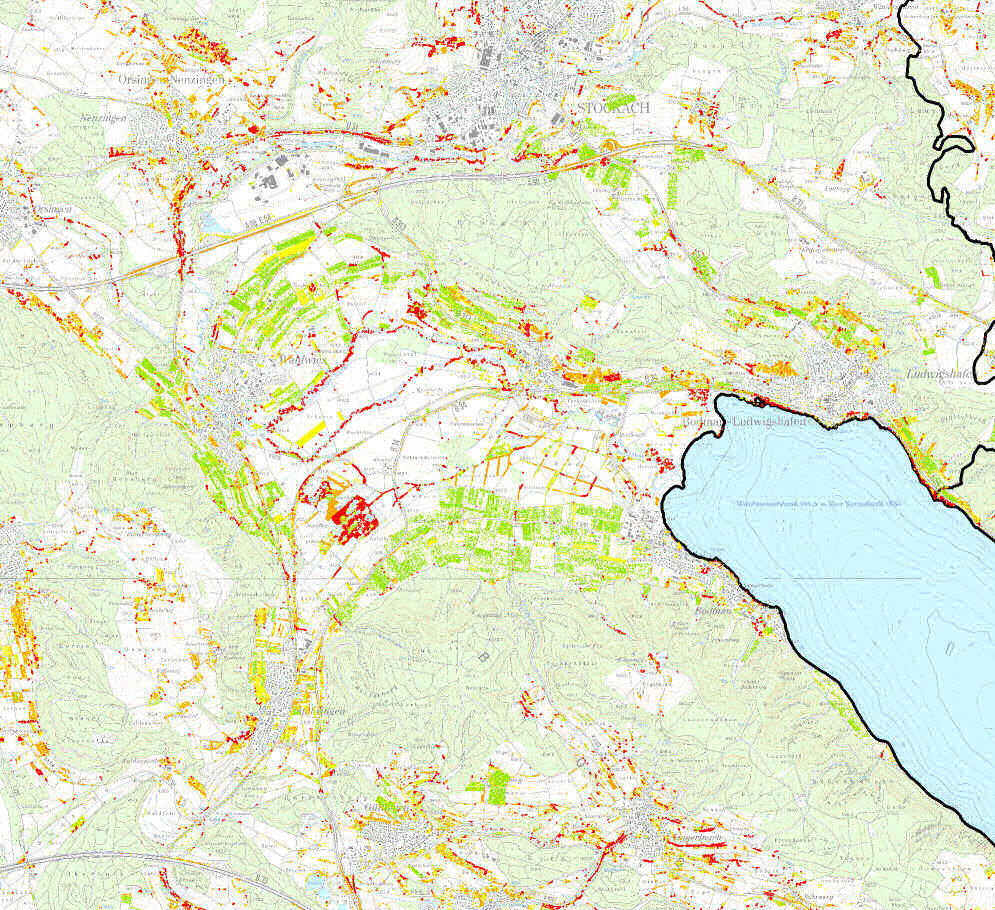
Abb. 7: Biomasse der Offenland-Gehölze bei Stockach (westlicher Bodensee)
Legende:
grün: 0 - 50 srm/ha
gelb: 50 -100 srm/ha
orange: 100 - 200 srm/ha
rot: 200 - 1000 srm/ha
Test Alpha-shapes (Eichen-Hasel-Wäldchen) als VRML (wrl)
-> Das Corona3D-Plugin wird benötigt:
www.parallelgraphics.com/products/cortona3d/
(für 64bit-Betriebssysteme die Version 7 beta installieren)
((Die folgende Abbildung entspricht Abb. 7 und sollte als interaktive drehbares 3D-Modell eingebunden werden.
Bei der Konvertierung von eps nach wrl gehen allerdings die Texturen verloren.))
Video: Ernteeinsatz mit einem
Moorraupenbagger: 40jährige Eschen-Baumhecke